メディカルバイオサイエンス学科
 大島 一彦(おおしま・かずひこ)
大島 一彦(おおしま・かずひこ)
Kazuhiko Ohshima
専門分野/分子進化学、再生ゲノム学研究キーワード/偽遺伝子、レトロポゾン、ゲノム進化
職位:教授
学位:博士(理学)(東京工業大学)
- 東京工業大学大学院生命理工学研究科博士課程修了
- 東京工業大学生命理工学部講師、同大学院生命理工学研究科講師を経て本学へ
研究テーマ
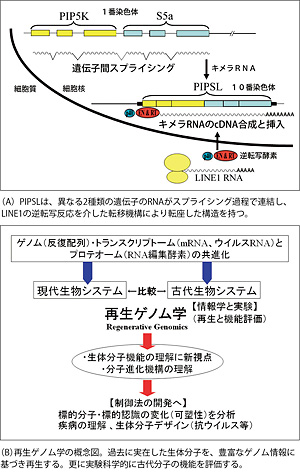
生物の世界では、普遍的な遺伝情報システムが、多様で複雑な生物・生命現象を存立させている。その不思議さに魅せられて、分子生物学や生命情報科学の手法を用いた研究をおこなっている。真核生物のゲノムに多量に存在する転移因子(RNAを介して移動する)の構造や転移機構をゲノム配列解析や培養細胞を用いて研究し、新たな転移機構モデルを提案した。また、ヒトゲノムに潜む偽遺伝子を全ゲノムから抽出し俯瞰的な分析をおこない、ヒトの祖先(霊長類)のゲノム内で、偽遺伝子が爆発的に増大した可能性を示した。 様々な生物階層(タンパク質立体構造、 発生・分化、生物進化など)とゲノム情報との因果律を理解することを夢見て、多様な切り口で研究を進めている。
(1)エキソン混成遺伝子の機能と進化
新機構(エキソン混成と遺伝子重複の連動)で誕生した若い遺伝子をヒトゲノムより見出した。リン脂質キナーゼとプロテアソームサブユニットの遺伝子が同一フレームで融合しており、翻訳産物はユビキチン化タンパク質と結合する。正淘汰(加速進化)を経ている。
(2)RNA編集機構の再生ゲノム学
多様な生理作用を示すRNA編集酵素に注目している。豊富なゲノム情報を活用し、現在は存在しない過去の酵素分子や標的分子を再生し、実験科学的に機能を評価する取り組みを始めた。
| 研究の応用領域 | 産官学連携で求めるパートナー |
|---|---|
| ヒトや家畜化(栽培化)動植物ゲノムの多型解析 反復配列を指標とした系統解析・種同定・個体識別 神経疾患の分子的な病理解明 |
個体や品種のゲノム情報に携わる研究者、企業 神経や生殖分野の基礎・臨床研究者、関連企業 |
Topics of research
My current research interests are molecular evolution of young genes, and evolution of RNA editing systems.
1. Molecular evolution and Population genetics on a novel retrogene created by domain shuffling
Domain shuffling has provided extraordinarily diverse functions to proteins. Previously, I and collaborators reported a unique mechanism of gene creation whereby new combinations of functional domains are assembled from distinct genes at the RNA level, reverse-transcribed and integrated into the genome by the L1 retrotransposon. The novel gene PIPSL, created by the fusion of phosphatidylinositol-4-phosphate 5-kinase (PIP5K1A) and 26S proteasome subunit (S5a/PSMD4) genes, is transcribed specif ically in human and chimpanzee testis. Our group is currently studying single-nucleotide polymorphisms (SNPs) of the young gene in human populations, and the molecular evolution of it in primate species to reveal how the newly combined domains were coordinated to create novel functions.
2. Evolutionary perspective of RNA editing enzymes
The subject of this research is on the function and the evolution of RNA editing enzymes, such as ADARs and APOBECs. ADARs (ADAR1-ADAR3) are closely related to the brain functions and diseases. The A→I RNA editing is catalyzed by the ADARs (adenosine deaminases acting on RNAs). The enzymes convert an adenine residue into an inosine residue by deamination. The A→I RNA editing is mainly found in the receptors and the ion channels which closely relate to the mental nerve functions of the central nervous system, e.g. the serotonin receptor, the glutamate receptor, the GABA receptor, and the potassium channel, etc. Therefore, the RNA editing is suspected to be a cause of mental diseases such as schizophrenia and depression. Actually, the RNA editing is reported to be a cause of ALS (amyotrophic lateral sclerosis).
We are examining the evolution of ADARs using abundant genomic information for a better understanding of the physiological functions of ADARs. The research will reveal the origins of various biological phenomena related to the A→I RNA editing. We are analyzing the genomic information with computers using the methods in bioinformatics and molecular evolution. Experimental researches on ADARs are also scheduled.
主な業績論文等
- Nishiyama, E., Nonogaki, M., Yamazaki, S., Nonogaki, H., Ohshima, K. Ancient and recent gene duplications as evolutionary drivers of the seed maturation regulators DELAY OF GERMINATION1 family genes. New Phytologist 230, 889-901 (2021)
- Matsumura, K., Imai, H., Go, Y., Kusuhara, M., Yamaguchi, K., Shirai, T., Ohshima, K. Transcriptional activation of a chimeric retrogene PIPSL in a hominoid ancestor. Gene 678, 318-323 (2018)
- Nishiyama, E. and Ohshima, K. Cross-kingdom commonality of a novel insertion signature of RTE-related short retroposons. Genome Biol. Evol. 10, 1471-1483 (2018)
- Ohshima, K. Parallel relaxation of stringent RNA recognition in plant and mammalian L1 retrotransposons. Mol. Biol. Evol. 29, 3255-3259 (2012)
- Ohshima, K. and Igarashi, K. Inference for the initial stage of domain shuffling: tracing the evolutionary fate of the PIPSL retrogene in hominoids. Mol. Biol. Evol. 27, 2522-2533 (2010)
- Babushok, D.V., Ohshima, K., Ostertag, E.M., Chen, X., Wang, Y., Mandal, P.K., Okada, N., Abrams, C.S., Kazazian, H.H.-Jr. A novel testis ubiquitin-binding protein gene arose by exon shuffling in hominoids. Genome Res. 17, 1129-1138(2007)






