小倉 淳 教授

小倉 淳
おぐら・あつし / Atsushi Ogura
職位
教授
学位
博士(理学)(総合研究大学院大学)
専門分野
ゲノム生物学、分子進化学
研究キーワード
生命情報、ゲノム、進化、多様性
所属
アニマルバイオサイエンス学科、ゲノム多様性研究室
バイオサイエンス研究科 分子バイオ科学技術領域
略歴
- 総合研究大学院大学博士課程修了
- JSPS特別研究員(PD)、 国立遺伝学研究所特任助教、 お茶の水女子大学特任助教、徳島大学講師を経て本学へ
研究室紹介・研究課題・実績
ゲノム多様性研究室
#生命情報 #ゲノム #進化 #多様性
地球上のすべての生命の起源は同じ。すべての生命が有する生命情報であるゲノム情報や発現遺伝子情報の比較から、生命の進化・多様性を探る研究をしています。ライフサイエンスとコンピュータサイエンス両方の素養を持ち、論理的思考を行える人材育成をめざします。

卒業研究テーマ例
- 選択的スプライシングの種間比較から迫る眼・脳神経系の進化
- 合成生物学・情報生物学によるクロレラ-ゾウリムシ共生システムの解明
- 新規医療用生物由来接着剤の開発とその生物学的獲得機構の解明
- 病気になる前の状態(未病)を発見するシングルセルトランスクリプトーム解析
生物の世界では、普遍的な遺伝情報システムが、多様で複雑な生物・生命現象を存立させている。その不思議さに魅せられて、分子生物学や生命情報科学の手法を用いた研究をおこなっている。真核生物のゲノムに多量に存在する転移因子(RNAを介して移動する)の構造や転移機構をゲノム配列解析や培養細胞を用いて研究し、新たな転移機構モデルを提案した。また、ヒトゲノムに潜む偽遺伝子を全ゲノムから抽出し俯瞰的な分析をおこない、ヒトの祖先(霊長類)のゲノム内で、偽遺伝子が爆発的に増大した可能性を示した。様々な生物階層(タンパク質立体構造、発生・分化、生物進化など)とゲノム情報との因果律を理解することを夢見て、多様な切り口で研究を進めている。
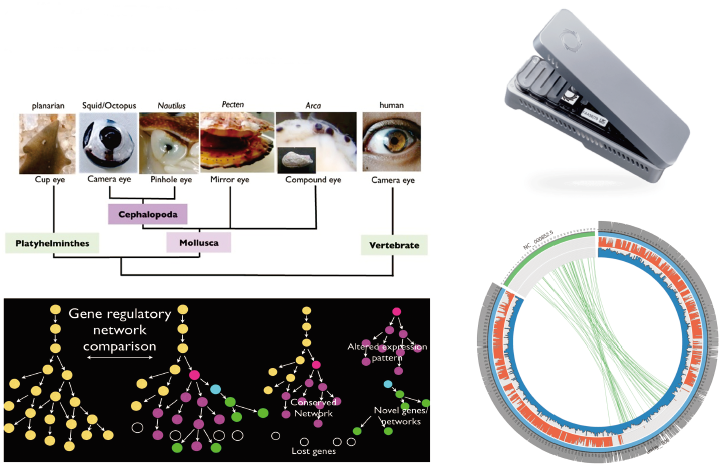
脊椎動物および無脊椎動物における眼・脳神経系の進化
様々な生物のもつ接着システムの進化
細胞内二次共生システムの初期進化
|
研究の応用領域 |
ゲノム解析技術を用いたゲノム医療・環境ゲノム |
|---|---|
|
産官学連携で求めるパートナー |
遺伝子資源探索およびその手法開発の関連企業・研究機関 |
To understand the species diversity and its evolutionary mechanism, we are focusing on the following topics:
Evolution of eye and central nervous system
The evolutionary study of eyes and brains aims not only at determining the evolution of the particular organs but also at understanding the role of the organs in the species evolution. There is a shared developmental process and a common gene regulatory network.
Evolution of adhesive molecules in various animals
Many organisms use glues. Biological adhesives can vary widely in structure and capabilities and often perform in ways that differ greatly from man-made adhesives. Studying biological adhesives can reveal their diversity and their function in nature.
Evolution of early stage of secondary symbiosis
Protists often retain symbionts such as algae. This phenomenon is key to understand the reason why photosynthetic organisms appear in deferent kinds of phyla.
|
1 |
*Yonezawa K., Nakata K., Minei R., *Ogura A. "DASE2: Differential Alternative Splicing variants Estimation method without reference genome, and comparison with mapping strategy", 2017, IJDMB |
|---|---|
|
2 |
*Komiyama T., Lin M., *Ogura A. "aCGH Analysis to Estimate Genetic Variations among Domesticated Chickens", 2016, BioMed Research International, 1794329 |
|
3 |
Kamijo A., Yura K., *Ogura A. "Distinct evolutionary rate in the eye field transcription factors found by estimation of ancestral protein structure" 2015, Gene, 555:2, 73-79 |
|
4 |
Yoshida M., Yura K., *Ogura A. "Cephalopod eye evolution was modulated by the acquisition of Pax-6 splicing variants", 2014, Scientific Reports, 4:4256 |
|
5 |
*Ogura A., Yoshida M., Moritaki T., Okuda Y., Sese J., Shimizu KK., Sousounis K., *Tsonis PA. "Loss of the six3/6 controlling pathways might have resulted in pinhole-eye evolution in Nautilus" 2013, Scientific Reports 3:1432 |
